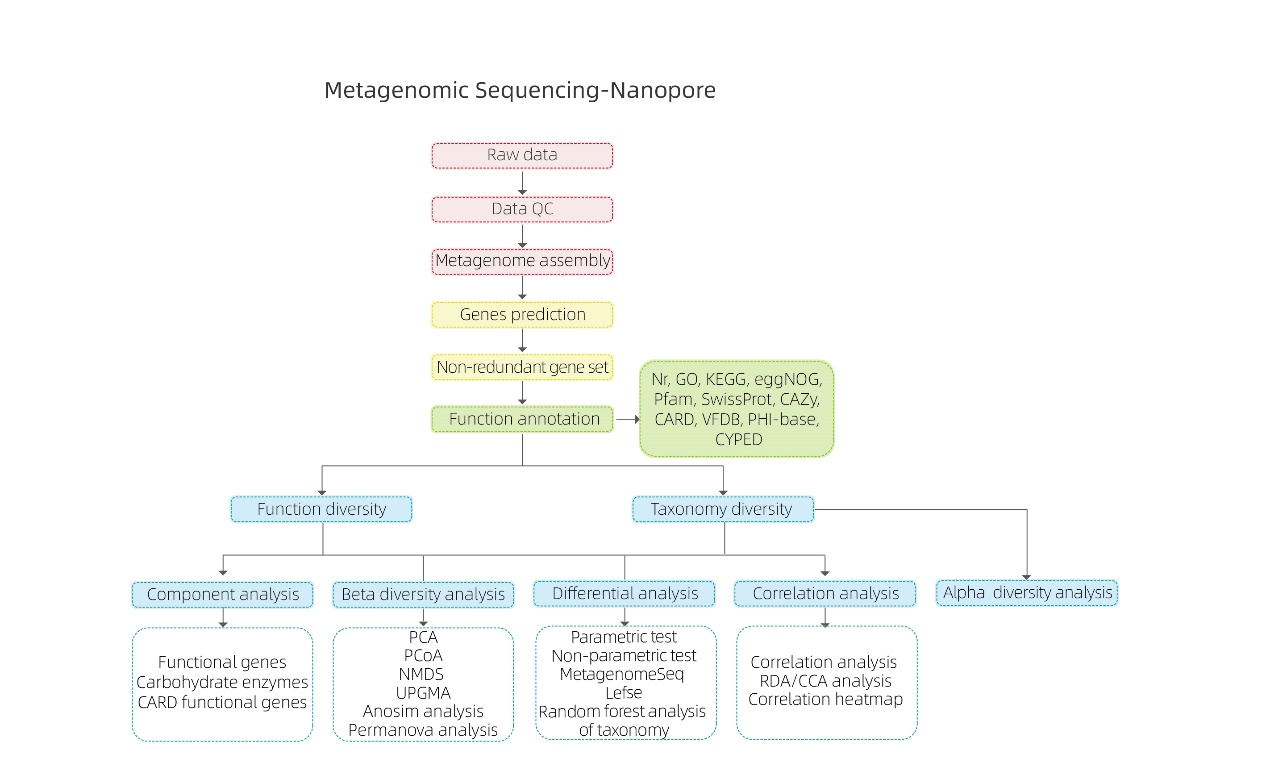
Metagenomic Sequencing-Nanopore
Service Virdeeler
● Héichqualitativ Assemblée-Verstäerkung Genauegkeet vun Arten Identifikatioun an funcational Gen Prediction
● Zougemaach bakteriell Genom Isolatioun
● Méi mächteg an zouverlässeg Uwendung a verschiddene Beräicher, zB Detektioun vu pathogene Mikroorganismen oder Antibiotikresistenz-verbonne Genen
● Comparativ metagenome Analyse
Service Spezifikatioune
| Plattform | Sequenzéieren | Recommandéiert Donnéeën | Ëmlafzäit |
| Nanopore | ONT | 6 G/10 G | 65 Aarbechtsdeeg |
Bioinformatik Analysen
● Raw Daten Qualitéitskontroll
● Metagenome Assemblée
● Net-redundante Genset an Annotatioun
● Spezies Diversitéit Analyse
● Genetesch Funktioun Diversitéit Analyse
● Inter-Grupp Analyse
● Associatiounsanalyse géint experimentell Faktoren
Prouf Ufuerderunge a Liwwerung
Prouf Ufuerderunge a Liwwerung
Sample Ufuerderunge:
FirDNA Extrakten:
| Beispill Typ | Betrag | Konzentratioun | Rengheet |
| DNA Extrakten | 1-1,5 μg | > 20 ng/μl | OD260/280= 1,6-2,5 |
Fir Ëmweltproblemer:
| Prouf Typ | Recommandéiert Proufprozedur |
| Buedem | Sampling Betrag: ca.5 g ;.Rescht verwinnte Substanz muss vun der Uewerfläch geläscht ginn;Grind grouss Stécker a passéiert duerch 2 mm Filter;Aliquot Proben am sterile EP-Tube oder Cyrotube fir Reservatioun. |
| Feeën | Sampling Betrag: ca.5 g ;.Sammelt an aliquot Proben an steril EP-Tube oder cryotube fir Reservatioun. |
| Intestinal Inhalt | Echantillon mussen ënner asepteschen Zoustand veraarbecht ginn.Wäscht gesammelt Tissue mat PBS;Zentrifuge de PBS a sammelt de Nidderschlag an EP-Réier. |
| Schlamm | Sampling Betrag: ca.5 g ;.Sammelt an aliquot Schlammprobe an engem sterile EP-Tube oder Cryotube fir Reservatioun |
| Waasserkierper | Fir Probe mat enger limitéierter Quantitéit vu Mikroben, wéi Krunnwaasser, Brunnwasser, asw., Sammelt op d'mannst 1 L Waasser a passéiert duerch 0,22 μm Filter fir Mikrobial op der Membran ze beräicheren.Späichert d'Membran an engem sterile Rouer. |
| Haut | Virsiichteg d'Hautoberfläche mat engem sterile Kotteng oder enger chirurgescher Blade schrauwen a se an engem sterile Rouer setzen. |
Recommandéiert Sample Liwwerung
Afréiere d'Proben a flëssege Stickstoff fir 3-4 Stonnen a späicheren a flëssege Stickstoff oder -80 Grad bis laangfristeg Reservatioun.Probe Versand mat Trockenis ass erfuerderlech.
Service Work Flow

Echantillon Liwwerung

Bibliothéik Bau

Sequenzéieren

Donnéeën Analyse

No-Verkaf Servicer
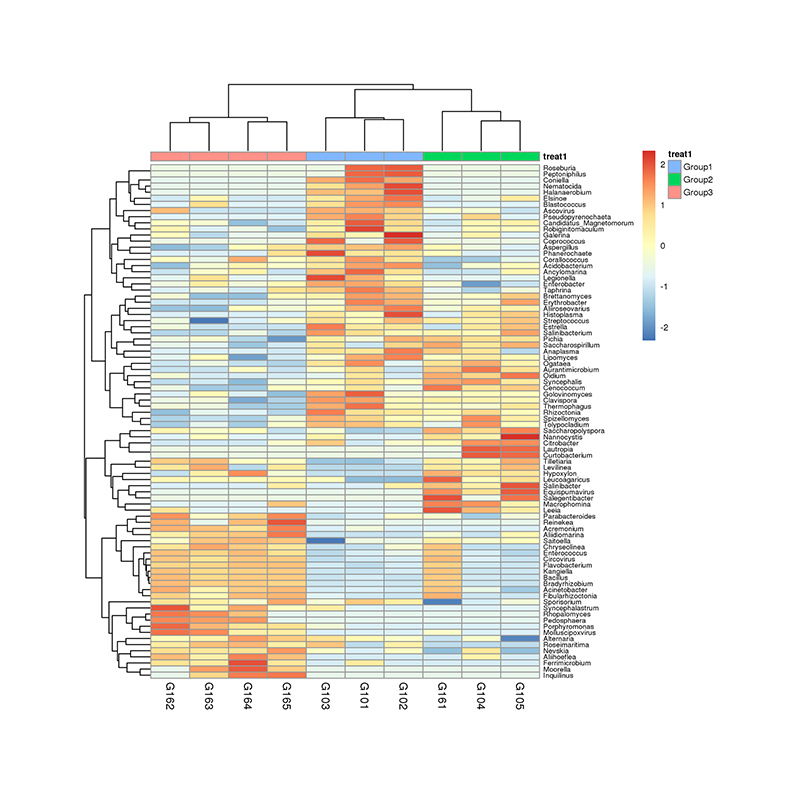
1.Heatmap: Arten Räichtum Clustering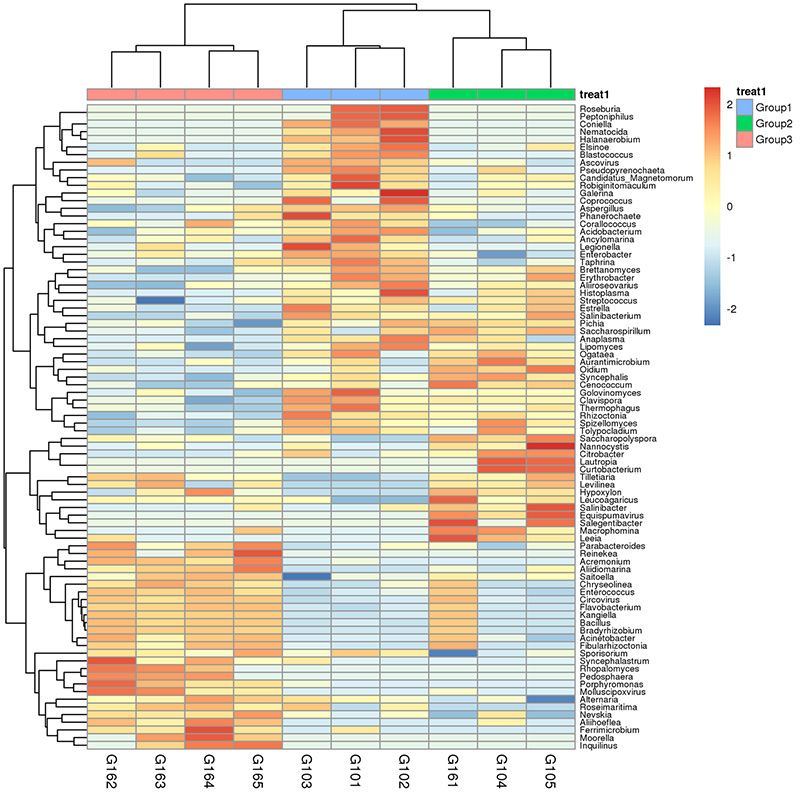 2.Funktionell Genen annotéiert op KEGG metabolesche Weeër
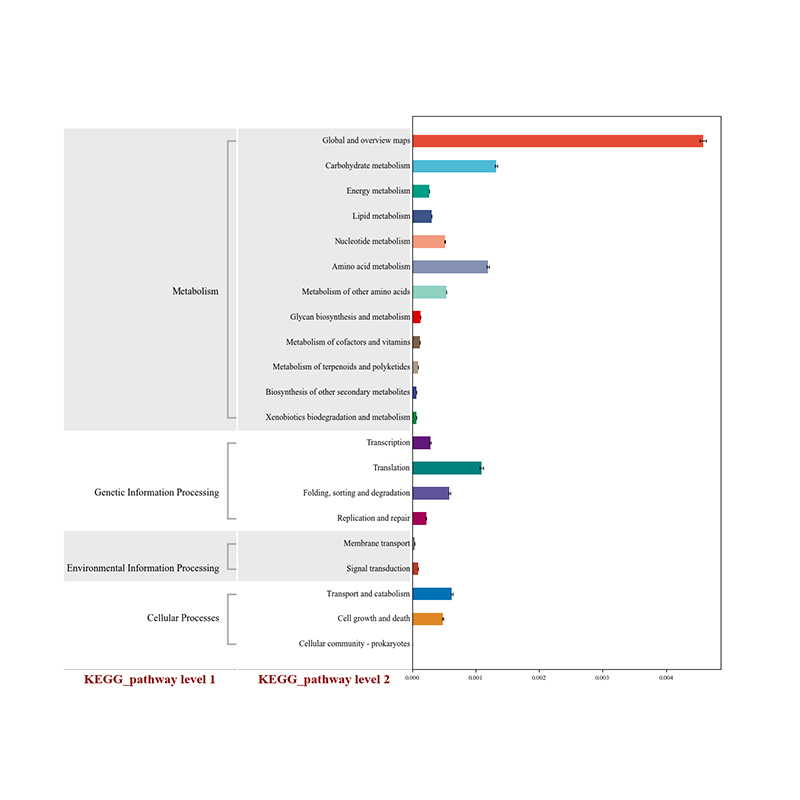
2.Funktionell Genen annotéiert op KEGG metabolesche Weeër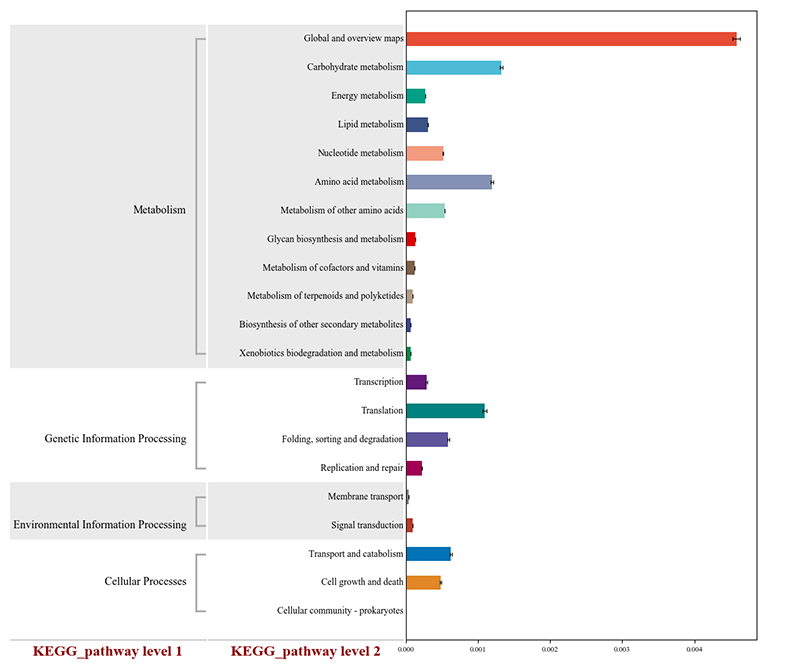 3.Spezies Korrelatioun Reseau
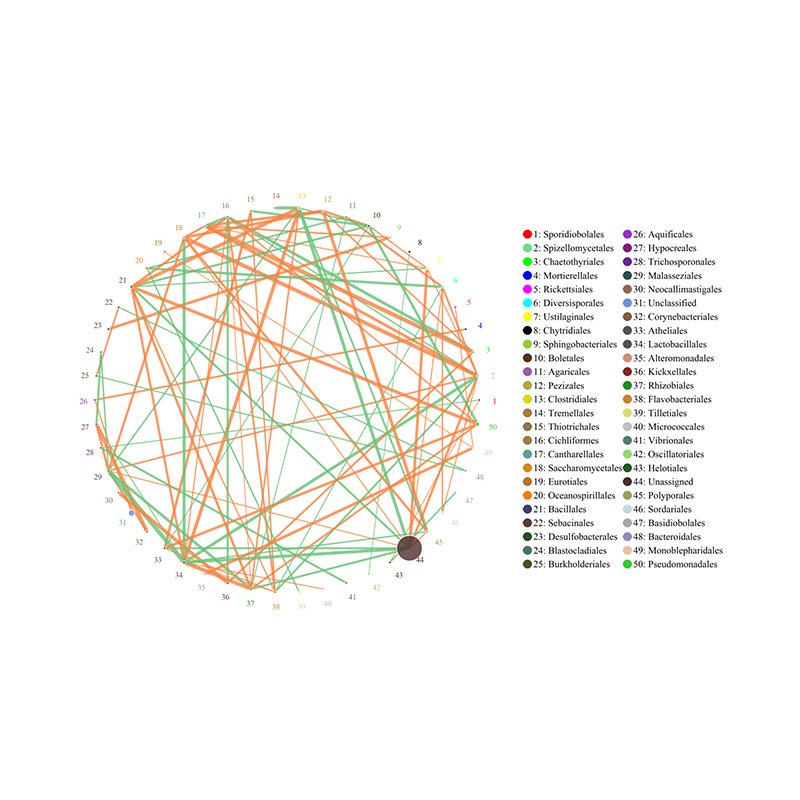
3.Spezies Korrelatioun Reseau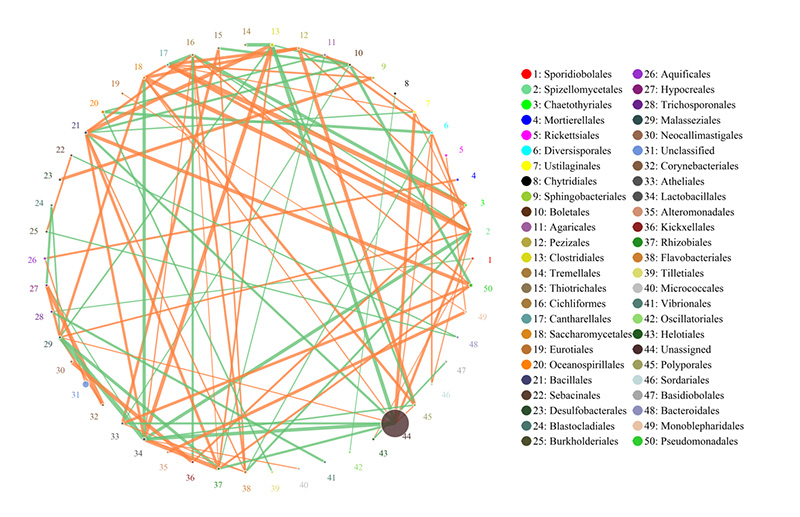 4.Circos vun CARD Antibiotike Resistenz Genen
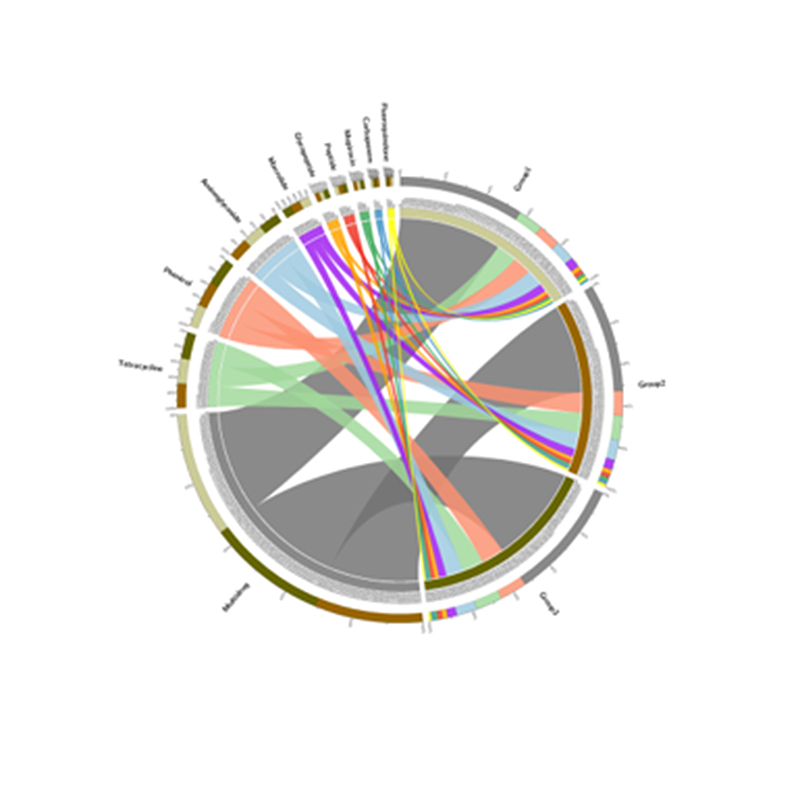
4.Circos vun CARD Antibiotike Resistenz Genen
BMK Fall
Nanopore Metagenomics erméiglecht eng séier klinesch Diagnostik vu bakterieller ënneschter Atmungsinfektioun
Verëffentlecht:Natur Biotechnologie, 2019
Technesch Highlights
Sequencing: Nanopore MinION
Klinesch Metagenomics Bioinformatik: Host DNA Ausschöpfung, WIMP an ARMA Analyse
Rapid Detektioun: 6 Stonnen
Héich Empfindlechkeet: 96,6%
Schlëssel Resultater
Am Joer 2006 huet déi ënnescht Atmungsinfektioun (LR) 3 Millioune Mënschen Doud weltwäit verursaacht.Déi typesch Method fir LR1 Pathogenerkennung ass d'Kultivatioun, déi aarm Sensibilitéit huet, laang Wendungszäit a Mangel u Leedung an der fréier Antibiotiktherapie.Eng séier a präzis mikrobieller Diagnostik ass laang en dréngende Bedierfnes.Den Dr Justin vun der University of East Anglia a seng Partner hunn erfollegräich eng Nanopore-baséiert metagenomesch Method fir Pathogenerkennung entwéckelt.Laut hirem Workflow kënnen 99,99% vun der Host-DNA entschäerft ginn.Detektioun vu Pathogenen an Antibiotike-resistente Genen kann a 6 Stonnen fäerdeg sinn.
Referenz
Charalampous, T., Kay, GL, Richardson, H., Aydin, A., & O'Grady, J.(2019).Nanopore Metagenomics erméiglecht eng séier klinesch Diagnostik vu bakterieller ënneschter Atmungsinfektioun.Natur Biotechnologie, 37(7), 1.